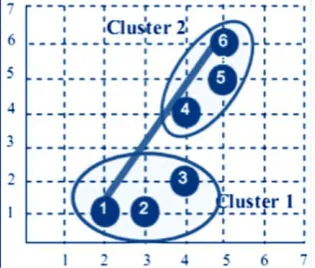
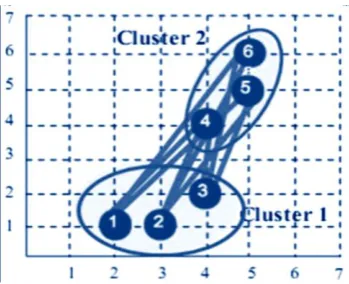
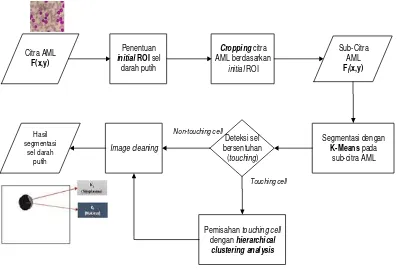
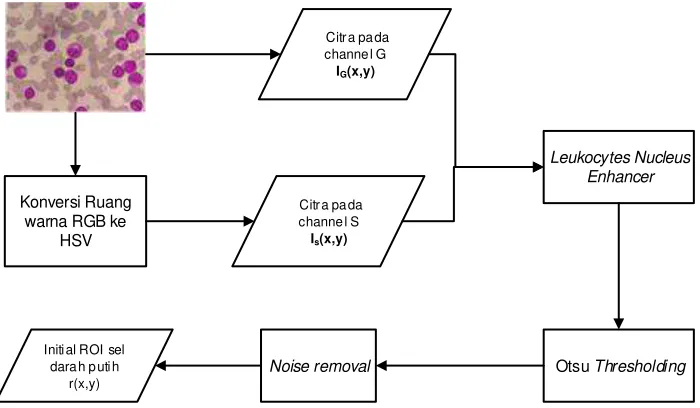
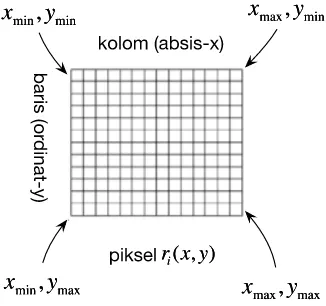
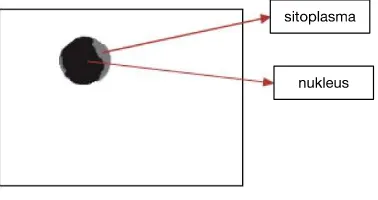
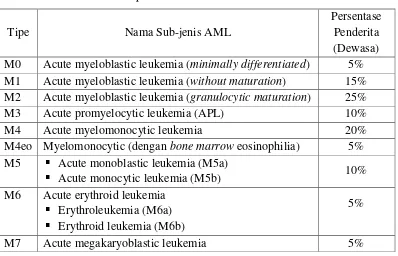
SEGMENTASI DAN PEMISAHAN SEL DARAH PUTIH BERSENTUHAN MENGGUNAKAN METODE K-MEANS DAN HIERARCHICAL CLUSTERING ANALYSIS PADA CITRA LEUKEMIA MYELOID AKUT
Teks penuh
Gambar
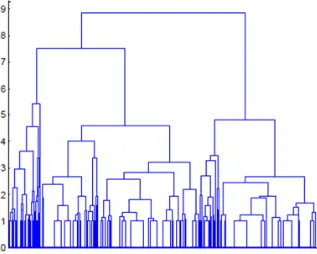
Dokumen terkait
Sedangkan jika perusahaan menggunakan pendekatan laba/rugi untuk mencatat transaksi beban dibayar di muka, misalnya beban asuransi untuk menampung asuransi yang
Untuk konstruksi atau struktur, pada umumnya, atap terdiri dari tiga bagian utama Untuk konstruksi atau struktur, pada umumnya, atap terdiri dari tiga bagian utama yaitu
No.. Pemasok diwajibkan melakukan registrasi berdasarkan formulir yang telah dipesiapkan oleh perusahaan agar terdaftar sebagai Pemasok resmi yang telah ditunjuk oleh PT.
Gagasan ekopolitik (ekologi-ekonomi-politik) kemudian muncul sebagai jawaban atas kritik tersebut yakni dengan memberikan sebuah cara pandang dalam melihat
Menimbang, bahwa pada pokoknya Penggugat mendalilkan bahwa rumah tangga Penggugat dan Tergugat awalnya rukun-rukun saja selama 3 bulan; namun setelah itu sudah tidak rukun
Analisa solvabilitas mengukur kemampuan perusahaan menutupi seluruh kewajiban-kewajibannya.Solvabilitas juga mengindikasikan jumlah modal yang dikeluarkan oleh investor dalam
Data primer yang di dapat berupa laju infiltrasi air ke dalam tanah dan nilai laju infiltrasi sebelum dan sesudah adanya lubang resapan biopori dan jumlah lubang resapan
Majoriti pelajar tidak mengetahui bahawa terdapat Piagam UKM Lestari, 2010 yang digunapakai bagi menjaga alam sekitar UKM iaitu seramai 209 responden (69.7%).. Berdasarkan