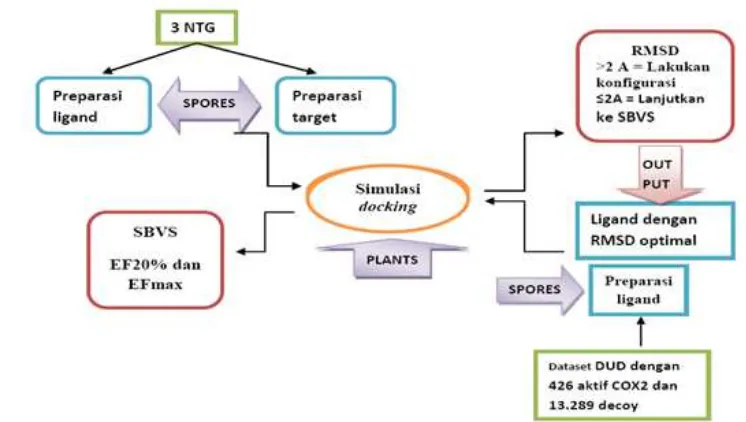
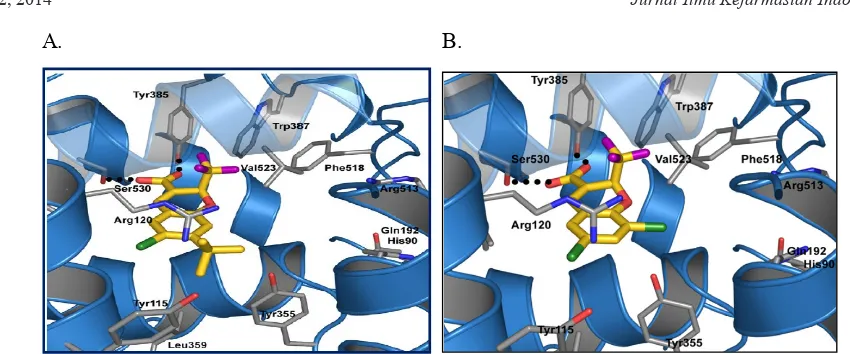
Konstruksi dan Validasi Protokol Skrining Virtual Berbasis Struktur dengan Kode PDB 3MQE, 3NTG, dan 3LN0 untuk Penemuan Inhibitor Siklooksigenase-2 (COX-2) (Construction and Validation of Virtual Screening Based on Code Structure of PDB3MQE, 3NTG, and 3LN
Teks penuh
Gambar

Dokumen terkait
Perawat yang mempunyai peran sebagai konselor, dimana perawat mempunyai andil yang cukup besar dalam memberikan informasi kepada remaja SMU tentang kesehatan reproduksi,
21 penyidikan suatu kasus narkoba yang dilakukan dengan tehnik pembelian terselubung ( undercover buy ) adalah dengan mengajukan rencana penambahan jumlah
Hasil uji-t menunjukkan bahwa terdapat perbedaan yang tidak signifikan (p>0,05) antara seleksi dan non-seleksi bobot badan starter (1 minggu) terhadap produksi
Kualitas nori daun pepaya dengan penambahan variasi tepung karaginan dengan parameter kimia (kadar air, kadar abu, kadar lemak dan kadar protein), mikro
Indikator untuk mengukur kemampuan pemahaman konsep menurut Lestari dan Yudhanegara (2017), diantaranya: 1) menyatakan ulang/kembali suatu konsep yang sudah.. dipelajari,
pencantuman tanda tangan. Hal ini penting adanya agar kontrak tersebut dinyatakan sah. Karena salah satu asas dalam perikatan adalah adanya konsensus atau kesepakatan. Namun
‘I can assure you,’ said the Major, ‘you and I are the only people in this part of the Tower.. The rest of the staff are attending