Teknik PCR-.
Teks penuh
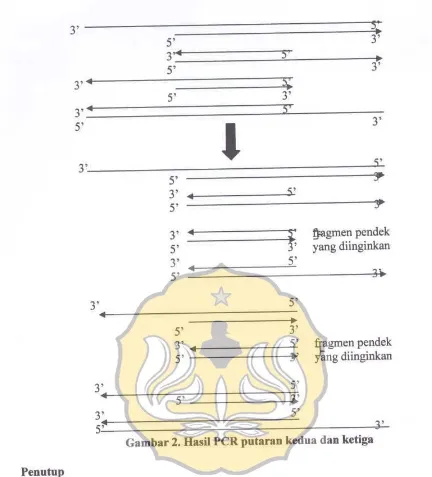
Gambar

Dokumen terkait
Jika dibandingkan dengan penelitian sebelumnya yang dilakukan oleh Budiono (2011) dengan menggunakan single cell water electrolyzer model spiral dimana didapatkan
Jika situs aktif yang terdapat pada permukaan adsorben karbon aktif belum jenuh dengan zat teradsorpsi maka dengan memperbesar konsentrasi logam Pb dan jumlah timbal
Dengan menggunakan metode efficient sequencing yang menerapkan algoritma Fuzzy C-Means clustering dan K-Means clustering pada hybrid recommender system diharapkan dapat..
Dari hasil evaluasi dengan analisis diskriminan dan analisis regresi dapat disimpulkan bobot peubah indikator kerentanan sosial-ekonomi yang terbaik adalah rataan..
Berdasarkan penelitian sebelumnya, peneliti mengusulkan pengembangan dari sistem yang telah dilakukan oleh Saleh, et al, yaitu dengan menambahkan metode implikasi
dari 0,05 berarti ada perbedaan yang signifikan kinerja mengajar guru yang sudah bersertifikasi dengan guru yang belum bersertifikasi serta ada perbedaan yang signifikan
Dalam segi promosi masalah yang terjadi adalah promosi yang dilakukan oleh perusahaan dianggap kurang, karena masih sedikit sekali distributor dan retailer yang menjual produk
Pengelolaan sampah adalah rangkaian kegiatan pewadahan, pengumpulan dan pengangkutan sampah ke tempat sampah sementara yang dilakukan oleh perusahaan RS